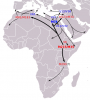
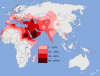
Vorsicht ist geboten, wenn man aus der heutigen Verteilung von Haplogruppen auf demografische Ereignisse in der Vergangenheit schließen möchte.
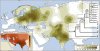
Grundsätzlich richtig. Im von Dir angesprochenen Fall - Ausbreitungsgeschichte von R1a - basiert die Karte (Inset unten links) jedoch nicht auf der heutigen Verbreitung, sondern auf der regionalen genetischen Diversität bzw. dem Vorkommen basaler Formen, also ohne späterere Mutationen und Aufspaltung in Untergruppen. Diese Methode ist für die Identifikation von genetischen "Urheimaten" allgemein gebräuchlich.
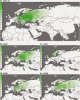
Auf dem gleichen Weg kommen die Autoren der von mir verlinkten Studie auch zur Feststellung, die in den weiteren Karten gezeigte Aufspaltung von R1a in einen westlichen und einen östlichen Zweig sei etwa um 4.000 v. Chr. in Ostanatolien " in the vicinity of present-day Iran" erfolgt.
Die Studie führt dann u.a. aus:
"To put our frequency distribution maps, PCA analyses, and autocorrelation results in archaeological context, we note that the earliest R1a lineages (genotyped at just SRY10381.2) found thus far in European ancient DNA date to 4600 years before present (YBP), a time corresponding to the Corded Ware Culture (..) This raises the possibility of a wide and rapid spread of R1a-Z282-related lineages being associated with prevalent Copper and Early Bronze Age societies that ranged from the Rhine River in the west to the Volga River in the east including the Bronze Age
Proto-Slavic culture that arose in Central Europe near the Vistula River (..) The corresponding diversification in the Middle East and South Asia is more obscure. However, early urbanization within the Indus Valley also occurred at this time and the geographic distribution of R1a-M780 (
Figure 3d) may reflect this."
Die "proto-slawische Kultur an der Weichsel" (um 2.600 v. Chr) ist so offensichtlicher Schwachsinn, dass es bei einem so renommieren Forscher wie Underhill eigentlich nur einen Grund für das Wörtchen "Slavic" geben kann..
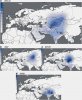
Für die östliche Verteilung, insbesondere in Zentralasien, fällt die hohe Korrelation mit bekannten Zentren des frühbronzezeitlichen Kupfer-und Zinnbergbaus auf. Das Bergbaumuseum Bochum hat da intensiv geforscht, bei Interesse könnte ich entsprechende Links raussuchen. Das "Indogermanen und Bronze"-Thema ist ja nicht ganz neu, und überzeugt mich auch mehr als die "Pferd und Wagen"-Geschichte (insbesondere vor dem Hintergrund, dass die ersten Wagenspuren in Flintbek bei Kiel gefunden wurden und der Trichterbecherkultur zuzuordnen sind, die ansonsten nicht gerade zu den heissen Anwärtern früher Indoeuropäisierung zählt).
Es müssen auf jeden Fall Untersuchungen an aDNA erfolgen und in die Betrachtung einbezogen werden
Klar, hat die verlinkte Studie ja auch gemacht, wie das obige Zitat zeigt. Eine umfassende, und laufend aktualisierte Darstellung aller Bestimmungen von aDNA findet sich hier:
Ancient Eurasian DNA of the Copper and Bronze Ages [
Schau Dir mal auf der "Silk-Road"-Seite die aDNA aus Xinjang, China an - 100% R1a. Was, bitte, sollen die ursprünglich aus dem Iran kommenden Jungs dort denn wohl gesprochen haben, wenn nicht Tocharisch?].
aDNA aus dem von dir genannten Bereich (Indus) ist derzeit noch nicht verfügbar und untersucht. Rückschlüsse aus der heutigen Verteilung von DNA in der Bevölkerung auf vergangene Bevölkerungsbewegungen können - wie gesagt - trügerisch sein. Die derzeit ältesten Funde von R1a und R1b stammen von osteuropäischen Jägern und Sammlern.
Letzteres steht hier, S. 5:
http://biorxiv.org/content/biorxiv/early/2015/02/10/013433.full.pdf
Zu der Studie wollte ich sowieso noch kommen. Haak ist grundsätzlich super - seine vorangegangene Studie (mit P. Brotherton) zu neolithischer mtDNA H war bahnbrechend, zeigte sie doch für Mitteleuropa (primär Elbe-Saale-Raum) massive Bevölkerungsumbrüche von Bandkeramik zu Rössen/ Lengyel, dann erneut mit dem genetischen Wiedererstarken der nordeuropäischen Jäger und Sammler in der Trichterbecherkultur, und im Endeffekt das fast völlige Aussterben der ersten mitteleuropäischen Neolithiker auf..Allgemein irritiert hat jedoch die Aussage dort im Abstract, um 4.000 v. Chr. sei die heutige mitteleuropäische genetische Struktur schon weitgehend geschaffen worden.
Neolithic mitochondrial haplogroup H genomes and the genetic origins of Europeans
In der von Dir verlinkten Studie behauptet er nun, nur ein Jahr später, vehement das Gegenteil, und zieht - auf sehr begrenzter Datenbasis - aus meiner Sicht teils voreilige, teils unfundierte Schlussfolgerungen.
Zu den Befunden im einzelnen (vgl. Table 2 bei Haak m Anhang, sowie meinen Link weiter oben):
R1a:
- ca. 5.200 BC, Karelien, Russland, mesolith. [R1a1, basal, entstanden vor iran. O-W-Aufspaltung, heute nur dokumentiert in Iran/ Türkei/ Kaukasus]
- ca. 2.600 BC, Eulau, Deutschland, Schnurkeramik [3 Funde, Vater und Söhne, R1a1, basal oder zu degen. für weitere Analyse]
- ca. 2.400 BC, Espenstedt, Deutschland, Schnurkeramik [R1a1a1, basal, vor iran. O-W-Aufspaltung]
- ca. 1.600 BC, Solenoozernaïa, Krasnoyarsk, Russland, Andronovo-Kultur [nur bestimmt auf basal R1a1a]
- ca. 1.600 BC, Oust-Abakansty, Khakassia, Russland Andronovo-Kultur [nur bestimmt auf basal R1a1a]
- ca. 1.100 BC, Halberstadt, Deutschland, Urnenfelder-Kultur ["balto-slaw."-Zweig, Z-280]
Hier gibt es im Grunde nichts Neues (Eulau, Espenstedt und die Andronovo-Kultur-Funde waren schon länger bekannt), ausser dem mesolithischen Fund aus Karelien. Der zeigt frühe Präsenz von R1 in NO-Europa an, allerdings in einer (erwartungsgemäß) basalen Form, und hat wohl wenig mit späteren Migrationen aus Ostanatolien/ Iran in die pontische Steppe und weiter zu tun.
R1b:
- ca. 5.300 BC, Derenburg, Deutschland, Bandkeramik [degeneriert, nur als P* ("Vatergruppe" von R) identifizierbar]
- ca. 5.250 BC, Samara, Russland, mesolith. Jäger/ Sammler
- ca. 5.100 BC, Els Trocs, Katalonien, Spanien (neol.) [2 Funde, lt. Haak Verwandte, zweiter Fund nur als yDNA P* markiert]
- ca. 5.000 BC, Derenburg, Deutschland, Bandkeramik [degeneriert, nur als P* identifizierbar]
- ca. 3.800 BC, Espenstedt, Deutschland, Baalberge-Kultur [degeneriert, nur als P* identifizierbar]
- ca. 3.500 BC, Quedlinburg, Deutschland, Baalberge-Kultur [degeneriert, nur als R* identifizierbar]
- ca. 3.200 BC, Samara, Russland, Yamnaya-Kultur
- ca. 3.100 BC, Samara, Russland, Yamnaya-Kultur
- ca. 3.100 BC, Samara, Russland, Yamnaya-Kultur
- ca. 3.100 BC, Samara, Russland, Yamnaya-Kultur
- ca. 3.000 BC, Ishkinova/ Orenburg, Russland, Yamnaya-Kultur
- ca. 2.900 BC, Samara, Russland, Yamnaya-Kultur
- ca. 2.800 BC, Samara, Russland, Yamnaya-Kultur
- ca. 2.550 BC, Kromsdorf, Deutschland, Glockenbecher-Kultur [2 Funde, mögl.verwandt]
- ca. 2.250 BC, Quedlinburg, Deutschland, Glockenbecher-Kultur
Das ist schon spannender - nicht so sehr der Jäger und Sammler aus Samara, sondern vor allem der spanische Neolithiker (der übrigens, bei der weiten Datierungsspanne der Samara aDNA, durchaus älter als diese sein mag). Bis jetzt hatten sich alle gefragt, wie es die vermuteten R1b-Indogermanen von der pontischen Steppe aus geschafft haben, die genetisch dominierende Haplogruppe am Atlantik zu werden (u.a. i90% in Wales, 88% bei Basken). Nun wissen wir, dass sie gar nicht aus der Steppe, sondern per Schiff aus Kleinasien kamen, und wohlmöglich auch gar keine Indogermanen waren (die Basken sind es ja heute noch nicht). Unterwegs sammelten die Els Trocs-Leute auch noch die Haplogruppe I2a1b1 an der dalmatischen Küste auf, was Haaks Anhang ebenfalls zeigt, er aber nicht weiter erwähnenswert findet.
Es wäre schön gewesen, wenn er versucht hätte, der stark degenerierten Bandkeramiker yDNA aus dem Elbe-Saale-Raum noch ein paar mehr Informationen zu entlocken, ob sie nun R1a oder R1b enthält - so bleiben nur Mutmaßungen (meine ist der tabellarischen Zuordnung entnehmbar).
Neu ist die Erkenntnis, dass die Yamnaia-Kultur offenbar stark durch R1b geprägt war, jedoch dort bislang die erwarte R1a yDNA-nicht augeftaucht. Das macht es aus meiner Sicht doch relativ unwahrscheinlich, dass die Schnurkeramiker von der Yamnaya-Kultur aus mit R1a beglückt, und in Folge indogermanisiert wurden.
Nimmt man alles zusammen:
- R1b-Ausbreitung nach Westeuropa durch die mediterrane, maritime neolithische Expansion, nicht durch die Steppe,
- Verwurzelung von R1a in Ostanatolien,
- Bislang kein Nachweis für R1a-Präsenz in der Yamnaya-Kultur, womit diese auch als Erklärung für das erstmalige Auftauchen dieser Haplogruppe bei den Schnurkeramiken fragwürdig wird,und
- Klare Ost-West-Trennung der jüngeren R1a-Untergruppen, ohne Überlappung nördlich des kaspischen Meers
halte ich die Kurgan-Theorie für genanalytisch widerlegt. Dass es um Renfrews anatolische Theorie kaum besser steht, weil die Bandkeramiker spätestens um 4.000 v. Chr. ausstarben, macht die Sache nicht einfacher. "Gehen Sie zurück auf Los, ziehen sie keine 4.000 Euro ein".
Was du mit "rückwandernden Ariern" meinst, bleibt unverständlich.
War tendenziell ein lautes Selbstgespräch angesichts des obigen Befunds. Noch sehr ins unreine gesprochen, erwäge ich folgendes Szenario:
- Proto-proto-indogermanisch existiert/ bildet sich im Indusraum, ist auch Ausgangspunkt der drawidischen Sprachen
- postglaziale Expansion nach Iran / Ostanatolien (grundsätzlich für Haplogruppe R1a genetisch belegt)
- dort Herausbildung des proto-Indogermanischen im Sprachkontakt mit afroasiatischen (akkadisch) und kaukasischen Sprachen
- ggfs, aber dann in begrenztem Umfang, Teilname an der neolithischen Expansion,
- Spezialisierung auf die Ausbeutung ostanatolischer Zinnvorkommen, ggfs. auch Teil/ Träger der Kura-Araxes-Kultur (Bronzeverarbeitung in Kleinasien nach neuen archäol. Befunden aus Israel bereits im 7.Jtsd. v.Chr.)
- Nach Erschöpfung ostanatolischer Zinnvorkommen Migration zu neuen Quellen, insbesondere Altai, Zentralasien, und den Ganges entlang Richtung Yünnan (Ostzweig), nach (Nord-)Westen hin zunächst Donauraum und Ural, dann weiter Richtung Alpen und Erzgebirge (Badener Kultur)
- "Rückkehr" nach Indien dadurch erleichtert, dass dortige dravid. Sprachen auf der selben Proto-Sprache basieren.
Out-of-India-Theorie ? Wikipedia
Kura?Araxes culture - Wikipedia, the free encyclopedia
Vin?a-Kultur ? Wikipedia
Badener Kultur ? Wikipedia
Danke für den schönen Link. Habe ihn überflogen, muss ihn aber noch mal in Ruhe lesen, gerade auch im Hinblick auf die vorskizzierten "Arbeitshypothesen".